結核・肺NTM症の網羅的な菌種同定が検体採取当日に可能に
急増する肺NTM症の診断迅速化に期待
研究成果のポイント
- 次世代シーケンシング技術を用いた新規診断手法「NALC-Seq法」を開発した。
- 検体採取当日に、180種以上の結核菌および非結核性抗酸菌(NTM)を、網羅的かつ亜種レベルまで特定可能にした。
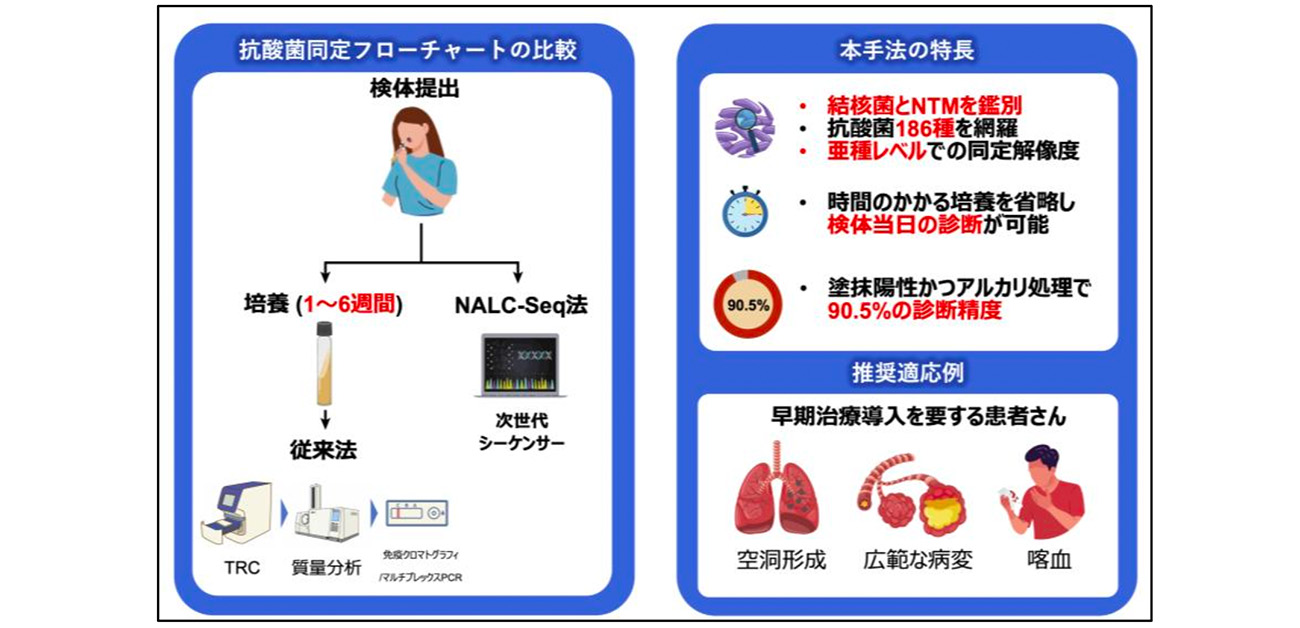
- 従来の同定法は1〜6週間の培養と複数の検査の組み合わせが必要であり、長い場合で約2ヶ月を要していた。本手法は培養を省略し、喀痰から直接同定することで、当日診断を実現した。
- 診断精度を高めるための検体前処理法(NALC-NaOH法)を特定し、塗抹陽性検体において90.5%という極めて高い正診率を達成した。本手法により、結核やNTM症の患者は、原因菌に応じた適切な治療を速やかに受けることが可能となる。
概要
大阪大学大学院医学系研究科呼吸器・免疫内科学 橋本和樹さん(博士課程)、同 福島清春 招へい教員、同微生物病研究所感染症メタゲノム研究分野 松本悠希 特任助教(常勤)、中村昇太 准教授らの研究グループは、大阪刀根山医療センターの木田博 呼吸器内科部長らと共同で次世代シーケンサーを利用した新しい抗酸菌診断手法(NALC-Seq法)を開発しました(図1)。
抗酸菌とは、今なお重要な結核菌と、200種以上に及ぶ非結核性抗酸菌(NTM)を含む細菌のグループで、症状や画像検査では両者の鑑別に難渋することも少なくありません。また、抗酸菌は菌種・亜種ごとに有効な治療薬や予後が異なるため、適切な治療を行うためには亜種レベルでの正確な同定が不可欠です。しかし、従来の検査法では迅速性と網羅性、亜種同定能の両立が難しく、複数の検査を組み合わせる必要があり、時間と手間を要しました。さらに、喀痰中の抗酸菌量は非常に少ないため、特別な培地で菌を培養した後に、菌の同定を行う必要があります。しかし、病原性を持つ抗酸菌の多くは発育が遅く、事前の培養に1〜6週間を要することが課題でした。
本研究では、次世代シーケンサーを用いて、培養工程を介さずに喀痰検体から直接、結核菌群および175種のNTMを網羅的かつ亜種レベルで同定する「NALC-Seq法」を確立しました。また、診断精度を最大化するために検体前処理工程を詳細に検討し、NALC-NaOH法が解析に有用であることを突き止めました。この最適化により、塗抹陽性検体において90.5%という高い正診率を達成し、また検体採取から1日以内という短期間での結果判明を実現しました。本研究が広く臨床現場で利用されるようになれば、臨床的に重要な結核の鑑別と、NTMの早期診断・治療導入が同時に可能となります。これまでの検査では約1〜2ヶ月を要していた同定が大幅に短縮され、感染症診療に大きな変容をもたらすと期待されます。
本研究成果は、米国の科学雑誌 『Journal of Clinical Microbiology』 に2026年2月27日に掲載されました。
図1. 次世代シーケンサーを用いた喀痰からの抗酸菌直接同定法の確立
研究の背景
肺NTM症は慢性進行性の難治性呼吸器感染症であり、世界的に増加しており、特に日本を含むアジアで多く報告されています。日本では2007年から2014年の7年間で、人口10万人あたりの罹患率が2.6倍増加し、現在では肺結核(Tb)をしのぐ罹患者数となっています。こうした背景から、迅速な診断手法の開発が求められています。
診断における大きな課題は2点です。1点目は、結果判明までに多大な時間と手間を要することです。患者さんから得られた喀痰検体は、セミアルカリプロテアーゼ(SAP)処理による溶解と均質化、雑菌処理(N-アセチル-L-システイン(NALC)-NaOH処理や酸処理)を行った上で培養検査へと進みます。培養検査は液体培養であるmycobacterial growth indicator tube (MGIT)培地もしくは固形培地である小川培地を用いて実施され、培養確認までMGIT法で2-4週間、小川培地で4-8週間を要します。喀痰から培養を行わずに直接同定が可能な手法として、PCR法、TRC法がありますが、これらは限られた数菌種のみに対応可能で、200種以上あるNTMを網羅的に同定することはできません。
課題の2点目は、日常臨床で同定できる菌種や亜種の範囲が限られることです。治療方針の決定には原因菌種・亜種の同定が重要ですが、従来の手法では網羅的かつ亜種レベルまでの正確な同定はできません。特に、近年増加している肺アブセッサス症の治療に当たっては亜種を個別に同定し、亜種ごとに治療を進めることが各種ガイドラインでも推奨されています。しかし、一般的な医療機関では個々の症例に対して亜種同定を行うことは容易ではありません。例えば、種同定において現在検査室で汎用されている質量分析法(MALDI-TOF-MS法)などでは、亜種を正確に鑑別することができず、種レベルの同定後に種ごとに異なる亜種同定検査をおこなう必要があります。加えて、症状や画像所見が類似する結核との迅速かつ正確な鑑別は、公衆衛生上の観点からも極めて重要ですが、従来の検査法では網羅性と迅速性の両立が困難でした。
図2. 従来法とNALC-Seq法の比較
研究の内容
研究グループは、結核菌群11種とNTM175種を網羅した大規模ゲノムデータベースと、抗酸菌特異的な遺伝子を選択的に増幅・濃縮するターゲットキャプチャーシーケンス技術を併用することで、喀痰提出から1日以内に亜種レベルでの網羅的同定が可能な「NALC-Seq法」を開発しました。
また、本手法の有効性を検証するため、前向き試験を大阪刀根山医療センターにおいて実施しました(図2)。115例の新規診断・既診断のTb/NTM症、および10例の非NTM症症例において前向きに検討した結果、亜種レベルの正診率は塗抹陰性例で13.9%、塗抹陽性例で75.4%でした。さらに、NALC-NaOHを用いた前処理が、酸処理よりも高い精度をもたらすことを突き止めました。この最適化により、NALC-NaOH処理かつ塗抹陽性例では、正診率は90.5%に達しました。塗抹陽性とは体内で抗酸菌の菌量が多いことを示し、ガイドラインでも治療開始の重要な指標として挙げられています。リアルタイム解析が可能な小型次世代シーケンサーを用いた場合、喀痰提出から診断までの時間は19時間と1日以内でした。
喀血や空洞形成を伴い、肺構造の破壊が急速に進行するリスクのある患者さんにおいて、結核も含めた鑑別と網羅的なNTMの同定を検体採取当日に完了できる本手法は、最適な治療を遅滞なく開始するために極めて高い有用性を持つと考えられます。
本研究成果が社会に与える影響(本研究成果の意義)
本研究成果により、結核菌および180種以上のNTMを1日以内に迅速かつ網羅的に同定できることで、患者は早期診断のみならず、病原体に応じた適切な治療を診断当日から受けられます。特に、公衆衛生上隔離が必要な結核も含めた鑑別と、適切な治療薬が異なるNTM亜種の特定を同時に、かつ培養を待たずに行える点は、感染拡大防止と予後改善の両面で大きな意義を持ちます。
また近年、次世代シーケンサーの開発・進歩により、小型かつリアルタイムにシーケンスが可能なMinIONが台頭し、病原体の迅速同定が可能となりつつあります。本研究の手法と最適化されたワークフローはこれらの小型デバイスに展開可能であり、高度な設備を持たない地域の医療機関においても、これまでの検査では得られなかったNTM亜種や株レベルの高精度情報の取得が可能となります。これにより、薬剤耐性の把握や伝播経路の推定に加え、いまだ謎の多いNTM症の病態解明に大きく寄与し、感染症診療の質を世界規模で底上げすることが期待されます。
特記事項
本研究成果は、2026年2月27日に米国科学誌「Journal of Clinical Microbiology」(オンライン)に掲載されました。
【タイトル】 “Comparison of Culture and Culture-free Methods for Comprehensive Identification of Mycobacteria: A Single-Center Prospective Study”
【著者名】Kazuki Hashimoto, Kiyoharu Fukushima, Yuki Matsumoto, Haruko Saito, Atsushi Funauchi, Nanako Hamada, June Yamauchi, Tadayoshi Nitta, Daisuke Motooka, Takuro Nii, Takanori Matsuki, Kazuyuki Tsujino, Keisuke Miki, Sho Komukai, Atsushi Kumanogoh, Shota Nakamura, Hiroshi Kida
参考URL
微生物病研究所 感染症メタゲノム研究分野
http://www.biken.osaka-u.ac.jp/laboratories/detail/19
用語説明
- 次世代シーケンシング技術
全ての生物が持つゲノムDNAはA(アデニン)、T(チミン)、G(グアニン)、C(シトシン)の4種類の塩基が連なった構造をしています。DNAの塩基配列を解読することはシーケンシングと呼ばれ、近年の技術革新が可能とした多量の塩基配列の同時解読技術を、特に次世代シーケンシング技術と呼びます。
- 非結核性抗酸菌(NTM)
マイコバクテリウム属細菌はグラム陽性細菌に分類される真正細菌の一属で、結核菌など約200種が登録されています。このマイコバクテリウム属の細菌は抗酸菌と総称され、そのうち結核菌群および、らい菌を除いた細菌を非結核性抗酸菌(NTM; Non-Tuberculous Mycobacteria)といいます。これらにより引き起こされる感染症はNTM症と呼ばれ、免疫不全患者だけでなく健常者にも感染し、感染後は自覚的な症状がほとんどないまま長い時間をかけて病状が進行します。発症後は咳・痰・血痰・発熱・食欲不振・体重減少・全身倦怠感などが見られ、抗生物質も効きづらいため、長期の適切な薬剤治療が必要となる難治性の病気です。
- 亜種レベル
生物の分類区分で、種の下位区分。非結核性抗酸菌症の主要な病原菌であるMycobacterium aviumの亜種であるhominissuis、silvaticum、paratuberculosisなど、近年次々と亜種が発見されています。
- PCR法、TRC法
PCR(Polymerase Chain Reaction:ポリメラーゼ連鎖反応)は、病原体のDNAの特定領域を増幅して検出する方法です。TRC(Transcription-Reverse Transcription Concerted reaction:転写逆転写協奏反応)は、病原体由来のRNAを等温条件で増幅して検出する迅速法です。いずれも短時間で結果が得られる一方、検出できる対象は検査であらかじめ定められた菌種や遺伝子に限られ、網羅的な同定には向きません。
- 結核菌群11種とNTM175種を網羅した大規模ゲノムデータベース
データベースに登録された配列と同定したい検体の配列を照合することによりマッチする菌種を探す手法はsequence typingと呼ばれ、それを複数遺伝子に拡張したものが Multi-Locus Sequence Typing と呼ばれます。菌種固有の遺伝子のDNA配列をデータベースに登録しておくことで極めて高い精度で同定が可能になり、データベースの規模が大きいほど検出能力が上昇します。今回、本研究においてはリボソーム分子の構成に関わる遺伝子や抗酸菌の抗生物質耐性に関わると考えられている184遺伝子を選んだ上で、公共データベースおよび本研究において新規に解読した11種の結核菌群、175種のNTM、計186菌種389亜種のゲノム情報を用いることで、マイコバクテリウム同定のための独自のデータベースを作成しました。
